Esta información ha sido obtenida de una publicación en ¡Cuánta razón! del pasado 28 de noviembre. Pero tenía que estar en este blog por lo que aporta.

Esto sí que es BIOINFORMÁTICA
Escuchando Puromac 191
el espacio web de @DoctorGenoma
Esta información ha sido obtenida de una publicación en ¡Cuánta razón! del pasado 28 de noviembre. Pero tenía que estar en este blog por lo que aporta.

Esto sí que es BIOINFORMÁTICA
Escuchando Puromac 191
En la sociedad en la que vivimos, el tránsito de los datos en internet es algo que no se mira con mucho hincapié. En este episodio del podcast de la comunidad JavaHispano, que generalmente trata de programación y no de leyes, tienen como invitado a Jesús Perez Serna, experto en Ley de Protección de Datos Personales y privacidad en general. El tema de la entrevista trata sobre qué consiste la Ley de Protección de Datos Personales y se opina sobre casos reales de resoluciones judiciales aplicadas. Lo bueno es que todo lo tratado lo explican con ejemplos del día a día y hace que, desde mi punto de vista, sea un programa de obligada escucha para concienciarse un poco de todo lo concerniente a la protección de datos.
Podréis suscribiros al podcast mediante este enlace o navegar por el post dedicado al podcast, que tiene un menú de enlaces muy interesantes y que completan la información que se da en este episodio sobremanera.
La semana del 8 al 21 de noviembre en León y Ponferrada se puede disfrutar de una de las actividades más interactivas en cuanto a la ciencia y tecnología se refiere: La semana de la ciencia.
Para este año se han enfocado en tres temas principales:
– Ciencia y tecnología de los alimentos: la ciencia en la cocina.
– Salud y calidad de vida.
– Biodiversidad.
La biodiversidad tiene un espacio especial puesto que nos encontramos en el año internacional dedicado a este tema.
Lo mejor de estas jornadas es, como he dicho antes, la interactividad. Hay un total de 9 actividades a disfrutar entre las que se incluyen multitud de talleres, entre los que destacan los culinarios como catas de vino y queso o también un taller de fisioterapia y otro dedicado a la memoria, y una visita a puertas abiertas en la Universidad de León.
Para que las jornadas fluyan sin problema, se ha habilitado un formulario de inscripción donde poderse apuntar. Esto es porque los aforos de los talleres y visitas es limitado. Así que, si se tiene ganas de asistir visitad la página web habilitada para ello y a apuntarse se ha dicho.

Este artículo lo escribo con cierta rabia e indignación, por debajo de la alegría de encontrar algo tan útil como este sistema operativo. Lo comento así porque llevo interesado en mejorar el estado de la bioinformática en este país (donde no hay una carrera o especialización como debería), ya que todos los estudios genéticos necesitan un soporte informático ya sea por un análisis de datos o por un estudio estadístico. Es como si los biólogos tuvieran miedo de meterse en la bioinformática. Pero lo curioso es que, en un congreso al que asistí este pasado verano, hablando distendidamente con grandes cargos de la sociedad española de genética ellos estaban también preocupados por el tema y discutimos la situación de este campo en España. La verdad es que somos pocos los biólogos que nos gusta trastear con los ordenadores y sacarles el máximo partido sin mandarles al carajo, pero la conclusión a la que llegamos es que deberían ser Biólogos y no informáticos los que desarrollaran una especialización en esta materia para poder adecuar mejor los datos a la realidad. Después de esta pequeña pataleta, el motivo de la entrada es mi “descubrimiento” de la nueva versión del sistema operativo Biolinux: la 6.0.
Esta distribución de Linux está basada en Ubuntu 10.04 y la desarrollaron para un público que necesita el uso de herramientas bioinformáticas para sus respectivos proyectos. El grupo que lo ha llevado a cabo es NERC Environmental Bioinformatics Centre y, para no tener que instalarlo de cero en usuarios que ya tengan Ubuntu en su ordenador, han posibilitado la instalación de todos los paquetes necesarios para que se transforme en BioLinux en cuanto a las aplicaciones se refiere. Esto es de gran ayuda puesto que muchos tenemos alojados en algún equipo ese sistema operativo y reinstalar de cero no es de mucho agrado.
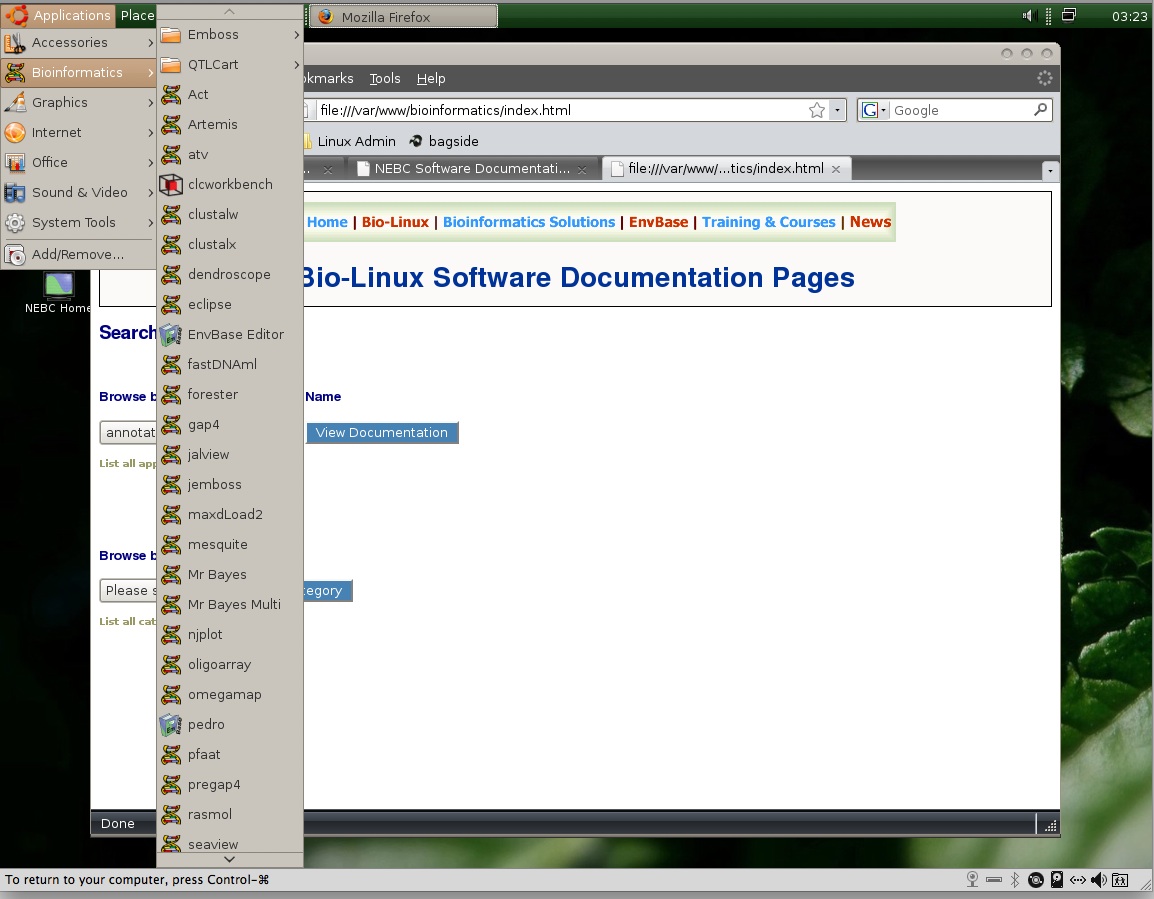
La única desventaja es que toda la documentación al respecto está en inglés, pero es algo asumible y que viene siendo habitual. Así se tienen aplicaciones instaladas como el QTLcartographer o CLCsequence viewer, que sirven para mapeo genético y manejo de secuencias. Así también, está adaptado para búsquedas para análisis como Blast. De todas formas AQUÍ está un listado con los paquetes instalados de serie con su descripción.
Siempre que hablo con biólogos que no usan más que güindous sobre sistemas Linux, son un poco esquivos a la hora de instalarlos. No tenéis que instalar el sistema operativo para probarlo con todas las funcionalidades. Estas distribuciones Linux vienen en modo Live, que significa que tan sólo tendréis que iniciar el ordenador (ya sea Mac o PC) para que arranque en el CD ó DVD donde se encuentre la distribución y podréis comprobar la potencia de este software libre.
Enlace de descarga de la distribución BioLinux 6.0
Escuchando: El Club vintage

Tras varios años como investigador me he topado siempre con un problema a la hora de escribir publicaciones y es el manejo de la bibliografía. Antes no se pensaba lo más mínimo en gestionar la bibliografía ayudándose de la informática más que para hacer listados para saber dónde se encontraban los papers o libros que servirían para completar un escrito. Ahora el volumen de la información es infinitamente superior. No hace falta escribir a un autor si se quiere tener su publicación. Las editoriales permiten la descarga, con “incentivos” o no dependiendo del artículo. Eso hace que se tengan que gestionar muchos más reseñas bibliográficas que antes.
Ahora bien, el problema llega a la hora de administrar todo lo recopilado. A la hora de descargar un artículo, en teoría viene etiquetado con un número de identificación llamado D.O.I. Esto facilita la clasificación ya que incluye en el archivo información como los autores, título, revista, año…etc. Pero no siempre es así. Debería ser un estándar a la hora de publicar on-line. Descartando este inconveniente de editarlo a mano, se pasa a añadirlo a la biblioteca de cada uno. Pues más vale editar cada artículo antes de guardarlo porque si no será un caos, ya que si te descargas el artículo suele tener un nombre tipo “fulltext.pdf” o “BMC124566.pdf”, nombres nada intuitivos para saber de qué va el paper. Por lo tanto necesitamos un gestor de bibliografía.
He podido trabajar con 3 gestores distintos: Papers, End note y Mendeley. El primero es específico para Mac y los otros dos son multiplataforma.
EndNote fue el primero que pude probar. No permitía la importación rápida de los artículos y se tenía que añadir toda la información a mano. Pero tenía una ventaja y era la perfecta integración con Microsoft Word para ir añadiendo la bibliografía eligiendo el formato de la misma. Pero había notables diferencias en las versiones para cada Sistema Operativo. Como habréis notado, me he referido en pasado ya que lo dejé de usar porque cuando se añaden a la biblioteca más de dos o tres artículos al día es bastante cansado ir etiquetando todo para que se pueda clasificar el artículo. Además, no permitía la reordenación en directorios como ya veremos más adelante. A todo esto hay que añadir la pega de que costaba alrededor de 300€ la licencia básica.
Mendeley parecía una buena opción al ser gratuito y permitir la importación de los artículos asumiendo el D.O.I.. Sin embargo sigue sin poder organizar las carpetas contenedoras de las publicaciones a nuestro antojo y la búsqueda de nuevos papers requiere una configuración nada intuitiva (o poco “user friendly” ;-D) y tampoco permite una exportación de la reseña fácil para añadirla a nuestro documento final.
De esta forma sólo me queda Papers. Tiene una gran pega y es que no se puede elegir el modo de generar la cita como en EndNote. Me explico. End note tiene una característica muy buena y es que permite generar una cita bibliográfica con el estilo de la revista científica que se desee. Por lo menos así era antes. De esta forma y al publicar un artículo, siempre se cumplía con las normas dictadas por la revista en cuestión sin errores ya que existían actualizaciones cada cierto tiempo. En Papers sólo existe una forma de exportar (por método de “copiar y pegar” y también “arrastrando y soltando” donde se quiera) y que tiene el gran fallo de que no añade toda la lista de autores, si no que sólo genera una cita con el nombre del primer autor más la coletilla “et al.” (es una locución proeniente del latin et alii que significa literalmente “y otros” pero que puede ser traducida como “y colaboradores”). A parte de este GRAN fallo, es la mejor interfaz de todas. También hay que decir que lo diseñaron unos científicos. Pero de eso ya os hablé en ESTE ARTÍCULO. Sólo quería destacar que aquí permite manejar todo en la misma ventana: buscar en distintas bases de datos, gestionar y buscar artículos de la biblioteca de cada uno e importar datos D.O.I. siempre que estén incluidos en el archivo pdf, haciendo que tan sólo en un clic se tenga el paper clasificado y perfectamente localizable puesto que permite ordenar los directorios a nuestro antojo: por fecha, año, editorial, autor…etc y en el orden que se quiera. Lo mejor, es el precio: 34€. Digo lo mejor porque merece la pena probarlo y ver las diferencias con Mendeley, que es el único que permite competencia por precio.
Lo bueno que tienen todos los gestores que he comentado es que el etiquetado del pdf permitirá siempre importar el paper a uno u otro software asumiendo toda la información. Siempre hago la misma comparación pero así se entiende mejor: es igual que la información que tienen los archivos de música que se ven en el display de los reproductores de mp3, detallándose la canción, autor, álbúm, letra…etc. pero en términos bibliográficos.
Al final de todo me he quedado con mejores sensaciones que años atrás, pero que me dejan mal sabor de boca. Parece que están jugando con nosotros. No se genera la aplicación definitiva de gestión bibliográfica y es muy, pero que muy necesario para que no se haga pesado el manejo de todos los artículos y lograr un mejor avance en ciencia.
Web de EndNote
Web de Mendeley
Web de Papers
Escuchando: Gravina 82 episodio 34
Para empezar, quería exponer la situación de esta enfermedad tal cual lo explican en Alzheimer Universal, centro de este artículo:
“La enfermedad de Alzheimer (EA) es una enfermedad degenerativa de las neuronas de caracter progresivo, de origen todavía desconocido, y frenta a la que no se puede, actualmente, ofrecer ningún tratamiento capaz de curarla o de prevenirla. Es la más frecuente de las demencias, la segunda causa de muerte en población de 65 años y más, y la primera causa de dependencia.
Afecta al 5-7% de la población de más de 65 años (cerca de 800.000 personas en nuestro país)y casi al 25% de los mayores de ochenta y cinco años, es decir, a esta edad, afecta a una de cada cuatro personas.
El número de personas afectadas se duplicará hacia el 2020, debido al envejecimiento continuo de la población, lo que convierte a esta enfermedad en uno de los problemas de salud más graves al que se enfrenta la Sociedad.
Esta enfermedad se manifiesta por perturbaciones progresivas de todas las funciones cognitivas aprendizaje, juicio, pensamiento, etc., El lenguaje, la coordinación de los gestos y las actividades diarias se hacen cada vez más difíciles hasta llegar a la incapacidad absoluta.
Entre el 85% y 90% de las personas afectadas vivien con sus familias, que llevan el peso físico, psicológico y económico al cuidarlas.”
La verdad es que alguna de las causas sí que se conocen, pero no voy a entrar en temas moleculares en esta ocasión. El verdadero problema de la enfermedad es que, y tan sólo en España, están afectadas alrededor de 2 millones y medio de personas. En éste cálculo se incluyen tanto los enfermos como los cuidadores. Y para mejorar la vida de todas esas personas se ha formado una agrupación llamada “Alzheimer Universal” que ha tenido la idea de compartir temas relacionados con ayudar a todo lo que rodea a esta enfermedad. Lo mejor es que son consejos prácticos para sobrellevar este gran problema. Además, se han servido de las redes sociales para abarcar más público y ya son casi 6000 las personas que apoyan la iniciativa en Facebook. También se encuetran en Twitter y tienen un canal de Youtube donde recopilan videos sobre esta enfermedad neurodegenerativa. Os dejo todos los enlaces para acceder a continuación. Iniciativas como estas hacen que sirvan verdaderamente para algo las redes sociales, no sólo como un parque de juegos y distracción.
WEb de Alzheimer universal
Twitter de Alzheimer universal
Facebook de Alzheimer universal
Canal de Youtube de Alzheimer universal
Este sitio web utiliza cookies para que usted tenga la mejor experiencia de usuario. Si continúa navegando está dando su consentimiento para la aceptación de las mencionadas cookies y la aceptación de nuestra política de cookies, pinche el enlace para mayor información. ACEPTAR