Las vacaciones hacen que nos volvamos perezosos. Y que nos lo pongan todo fácil para seguir la ley del mínimo esfuerzo. Qué mejor que las webinars para estar al tanto de las técnicas que presentan ciertas marcas comerciales. En este caso os LI-COR Biosciences tiene un surtido de webinars que se pueden visionar y compartir con compañeros de trabajo a los que les pueda interesar. Para tener los conceptos claros, un webinar es un seminario virtual al cuál se accede vía web. Son presentaciones con cierta interacción, ya que se pueden hacer preguntas sobre las dudas que surjan a lo largo de las presentaciones.
En estos webinars, LI-COR Biosciences nos muestra sus tecnologías y cómo sacarles partido. Verdaderamente no son más que presentaciones comerciales, pero pueden dar ideas para avanzar en los diferentes campos de investigación. Os dejo el enlace de la página que contiene el menú de los vídeos. ¡Hala! a hacer clic y ver las películas.
Blog
El riego en la Universidad de León parte 1
Este es uno de los numerosos posts que publicaré sobre la gran gestión del agua destinada a la jardinería en la ULE. Estas son imágenes de un edificio anexo a donde trabajo.
AgileMedSearch y Personal Genomics como aplicaciones en potencia
Parece que el mundo de la tecnología móvil y la ciencia comienzan a darse un poco más la mano. Después de la gran aplicación del grupo Mekentosj para iPhone llamada “Papers” para la gestión de artículos y separatas (cuya aplicación para Mac la tengo catalogada como indispensable en mi Macbook), comienzan a abrirse nuevos caminos para sacar partido a “la nube”.
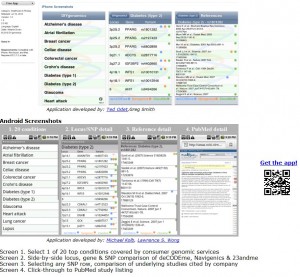
AgileMedSearch es una aplicación que permite realizar búsquedas en la base de datos de PubMed y nos muestran los resultados de los estudios relacionados con nuestra búsqueda. De cada estudio sólo se puede leer el resumen o “abstract” y contactar por e-mail con los responsables del artículo, pero algo es algo. Por ahora sólo está disponible para Android. Os dejo el código QR de descarga a continuación.

La aplicación “Personal Genomics” no es más que un programa que sirve para mostrar los estudios realizados por 3 compañías de genómica destinadas a dar servicio de análisis para estudios genéticos. Estas compañías son deCODEme, Navigenics y 23andme. Tan sólo se muestran las referencias de los loci estudiados para 20 enfermedades humanas. Os dejo una imagen de la aplicación tanto para iPhone como Android y el código QR para los “Androides” que la quieran probar.
Escuchando: Podcast de Soy-friki número 13
La identidad de los virus intestinales
A diferencia de los virus que nos enferman, estos virus no son depredadores. De hecho, la mayoría de ellos quieren tener una existencia agradable dentro de las bacterias que viven en el intestino. Aquí, el virus se considera que influye en las actividades de los microbios del sistema digestivo, que entre sus otros beneficios nos permiten digerir ciertos componentes de nuestra dieta, tales como hidratos de carbono de origen vegetal, que no lo podríamos hacer por nuestra cuenta. Además, los virus pueden actuar como un sensor para medir la salud general de la comunidad microbiana intestinal, ya que responden a los estreses y se recuperan después de una enfermedad o intervención terapéutica.
“Los virus son los principales depredadores en el planeta Tierra”, dice el autor principal Jeffrey Gordon, director del Centro de la Universidad de Washington para las Ciencias del Genoma y Biología de Sistemas, cuya investigación pionera ha proporcionado una comprensión de la naturaleza de los microbios que viven en nuestro intestino: cómo se adquieren y cómo nos benefician, incluyendo su influencia en la nutrición.
“Gran parte de la información que tenemos acerca de los virus que conviven con las bacterias provienen de estudios de los hábitats del medio ambiente, como los océanos”, dice Gordon. “Allí, el estilo de vida de los virus puede ser descrito como una dinámica “depredador-presa”, con una batalla continua en la evolución de los cambios genéticos que afectan a los virus y sus huéspedes microbianos. Una batalla que da forma a la estructura y dinámica de las operaciones de estas comunidades microbianas. Queríamos conocer la naturaleza de los virus y su forma de vida en la comunidad microbiana más abundante que habita nuestro cuerpo, la de nuestro intestino.”
En el nuevo estudio, liderado por el estudiante de posgrado y becario Fulbright Alejandro Reyes, los científicos descifraron el ADN aislado de los virus en muestras de heces proporcionados por cuatro parejas de gemelos idénticos y sus madres. Los investigadores secuenciaron el ADN viral a partir de muestras de heces tomadas en tres momentos diferentes durante un período de un año, lo que les permitió seguir cualquier fluctuación en las comunidades virales. Los investigadores también secuenciaron el ADN de todos los microbios de las muestras de heces de las mujeres, que les permitían comparar las comunidades microbianas y virales en el intestino.
Sorprendentemente, más del 80 por ciento de los virus en las muestras de heces no se había descubierto previamente. “La novedad de los virus fue evidente de inmediato”, dice Gordon. A cada individuo (por separado) en el estudio, se le asignó una “huella genética” viral correspondiente al análisis de cada uno de los virus encontrados en el intestino grueso. El viriomas (genomas virales) intestinales de los gemelos idénticos eran tan diferentes como el viriomas de individuos no emparentados. Esto contrasta con las bacterias intestinales. Cuando los investigadores observaron a las comunidades de bacterias en las muestras de heces, encontraron que los miembros de la familia compartían, en cierto grado, las mismas especies microbianas.
A pesar de las variaciones distintivas en las comunidades viral de una persona a otra, los investigadores descubrieron que la especie viral predominante en el tracto gastrointestinal inferior de cada individuo se mantuvo estable genéticamente en el período que duró el estudio (un año). Esto difiere de las comunidades bacterianas, que experimentaron mayores fluctuaciones. En otras palabras, los virus de ADN en las muestras de heces no parecían mostrar el estilo de vida “depredador-presa” de las comunidades que se observaban en otros ambientes.
Los investigadores planean ahora estudiar los virus en los intestinos de los gemelos idénticos en desarrollo infantil de diferentes familias para determinar cómo se instalaron inicialmente los virus en el ecosistema intestinal y la forma en que se ven influidas por el estado nutricional de sus huéspedes humanos . Además, para comprender mejor los estilos de vida viral en toda la longitud del intestino, se están introduciendo estos virus en ratones que sólo contienen microbios del intestino humano.
En los últimos años, una serie de proyectos en todo el mundo han iniciado la catalogación de los microbios que viven dentro y en el cuerpo humano, con el objetivo de entender la relación entre las comunidades microbianas, la salud general y la enfermedad. La nueva investigación sugiere que dichos proyectos también deben dirigir su atención a los virus que coexisten y co-evolucionan con las bacterias y otros microbios que normalmente viven en nuestros cuerpos.
Como curiosidad, para la secuenciación del genoma viral utilizaron el sistema de pirosecuenciación Roche 454, obteniéndose un dato total de más de 280 millones de nucleótidos.
Referencia: Revista Nature
Mesa para ver el Mundial
La verdad es que en estas fechas comienza a haber escasez científica. Y más con el calorcito que hace. Ya que España ha llegado a las semifinales, seguro que han surgido más forofos de la ROJA y todos se reunirán alrededor de una mesa con los refrescos y snacks preferidos para disfrutar del partido del Miércoles. Pues qué mejor que fabricar una mesa personalizada mundialista para el momento.
Como se ve en la imagen, lo único malo es disponer de 4 balones iguales en dimensiones (si no se quiere usar la fregona muy a menudo, claro). Lo mejor es que en la web que enlazo a continuación vienen las instrucciones detalladas para su fabricación.
Las banderitas que hay al lado de la tele presagiaban un duelo hispano-germánico…jejeje.
Web de referencia: Manualidades.tv
Copiar y pegar en los genes
En un artículo publicado en la revista Cell, el Dr. Richard Placa y sus colaboradores examinaron retrotransposones L1 (o LINE-1): secuencias de ADN que pueden “copiar y pegar” su código genético por todo el genoma. Al romper los genes, las L1 pueden ser responsables de algunos casos raros de enfermedades genéticas.
Trabajando en colaboración con colegas de las Universidades de Michigan y Washington, los investigadores desarrollaron una técnica innovadora para las L1, utilizando secuencias cortas de ADN llamados fósmidos. Estos son fragmentos de ADN circulares que pueden ser introducidos fácilmente en las células bacterianas y transportar fragmentos de ADN humano.
Cada fósmido sólo puede tener una cantidad específica de ADN, aproximadamente 40.000 pares de bases. Así, comparando los dos extremos de un trozo de ADN humano introducidos en un fósmido, comparando sus posiciones conocidas en el * secuencia del genoma humano, los científicos fueron capaces de encontrar in situ diferencias de tamaño de forma rápida y sencilla.
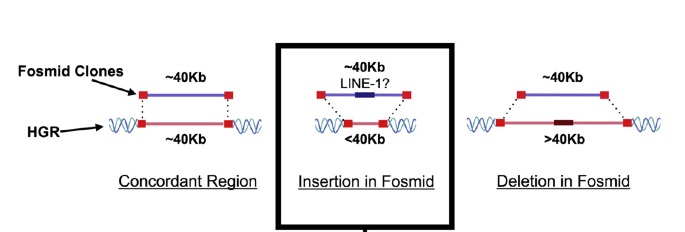
Una vez identificadas las inserciones, el siguiente paso era ver si podían “saltar” en los cultivos de células humanas y su frecuencia, que es donde el equipo de investigación encontró algo completamente inesperado.
“Estudios previos han sugerido que gran cantidad de las L1 debe saltar, pero no”, dice el Dr. Placa. “Alrededor de la mitad de las L1 saltan realmente, que era muy sorprendente. Además, hemos encontrado alrededor de 65 elementos, que no habían sido previamente identificados. Esto nos dice que la activación de retrotransposones humanos es mucho más común de lo que se esperaba. Los retrotransposones individuales activos de tipo L1 son muy raros, pero hay gran cantidad de ellos”.
El documento “LINE-1 Retrotransposition Activity in Human Genomes”, escrito por Beck y colaboradores, es uno de los tres estudios sobre los L1 publicados en la edición del 25 de junio 2010 en Cell. Según dicen los trabajos, 38 de los 65 elementos móviles estudiados son activos, lo cuál es sorprendente.
Debido a la creencia errónea de su rareza, los retrotransposones activos no han sido estudiados tan de cerca como otras fuentes de variación genética. Son porciones grandes de ADN que cuando saltan en un gen pueden alterar la secuencia genética y esto puede causar una enfermedad.
A modo de curiosidad, quería observar que en maíz el 49-78% de su genoma está formado por retrotransposones. En trigo, alrededor del 90% del genoma son secuencias repetidas y el 68% son elementos transponible. En mamíferos, casi la mitad del genoma (del 45% al 48%) lo comprenden transposones y remanentes de transposones.
Fuente: Revista Cell

